尔云间 一个专门做科研的团队

小果今天给大家带来的是Cytoscape的相关使用方法,Cytoscape是一个用来美化蛋白互作网络的工具,相信很多小伙伴已经掌握了Cytoscape的基本使用方法,那今天就让我们来进阶一下吧,用Cytoscape来计算一下蛋白互作网络的各个指标。

Cytoscape是可以安装各种插件来帮助我们工作的,今天我们要用到的插件是cytoHubba,安装方法是点击左上角apps里的app Manager。
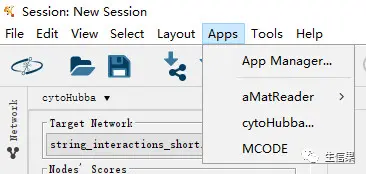
然后从下面的界面中找到需要安装的插件。
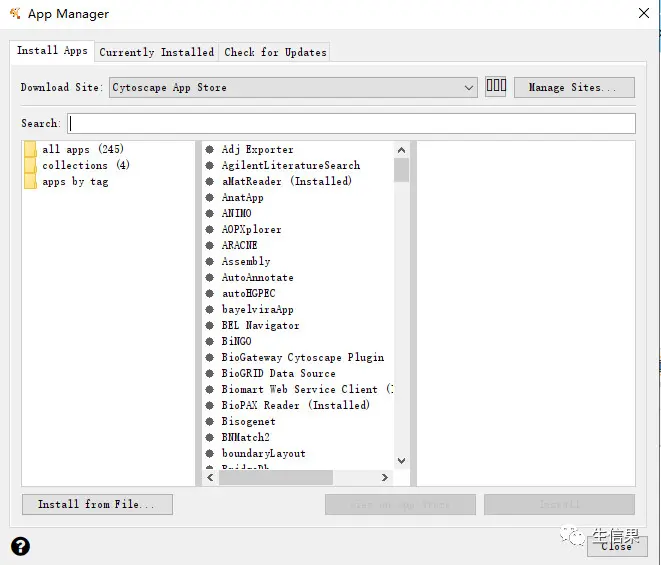
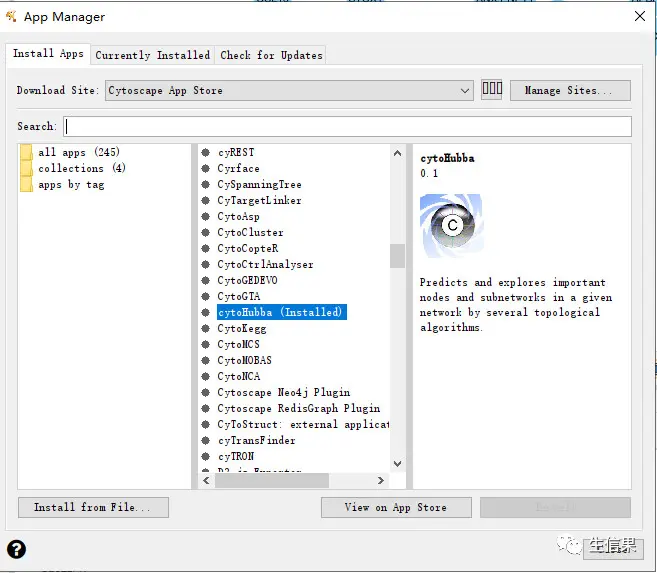
找到安装就行了,小果这个就是已经安装好了。
安装好之后在软件的最左侧就能找到cytoHubba这个按钮,点一下,就是下面这个界面。
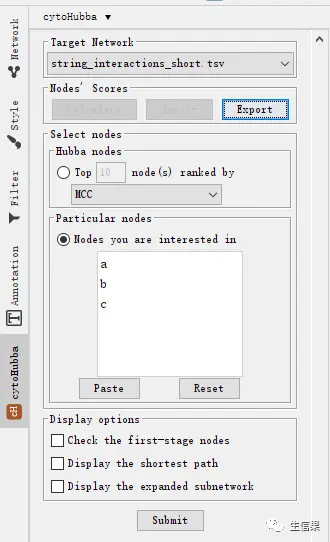
这里小果是已经点了calculate这个按钮,点击之后就会计算蛋白互作的各个指标。
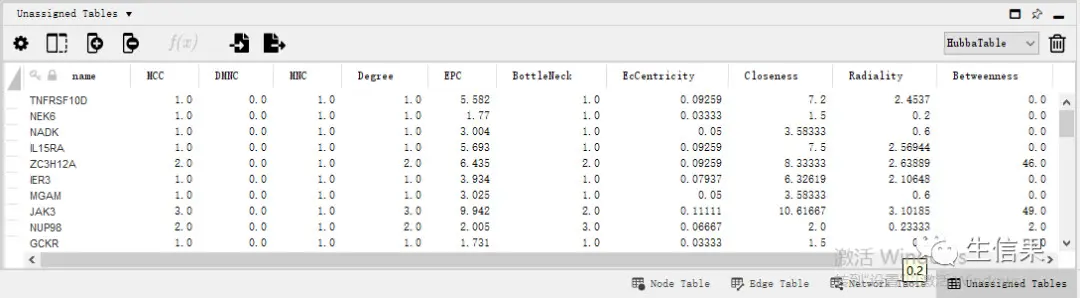
这个数据可以直接导出,但顺序可能会发生些变化。
得到这些数据之后就可以筛选我们想要的蛋白互作网络的节点基因了。
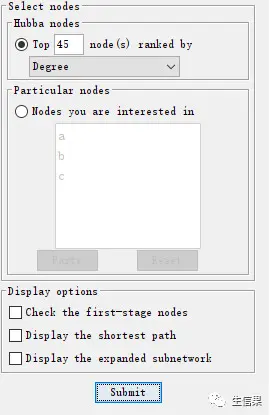
这里可以选择按照指标排序,按照顺序填充颜色,颜色越深,数据越大。小果这里选择的是degree,也就是节点上链接的线的数量。
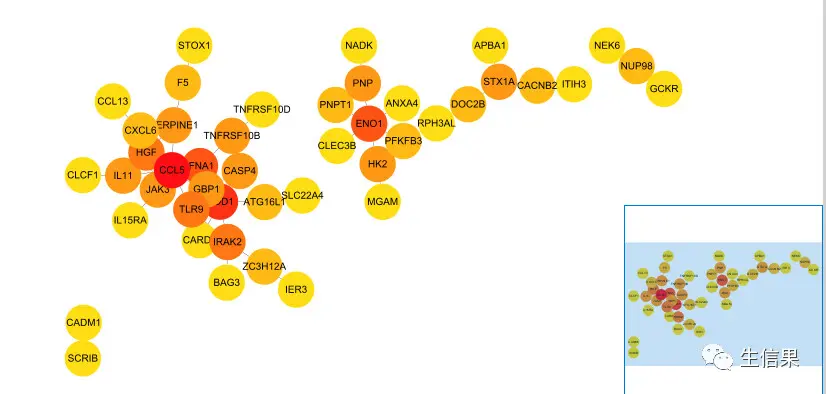
画出来大概就是这样的。当然了,小伙伴们也可以选择其它指标,比如说MCC,MNC,EPC等等。
好了,这就是今天的主要内容了,小伙伴们感觉如何呢,小果觉得这些还是比较实用的,极大的美化了蛋白网络互作图。小伙伴们还有什么问题欢迎来和小果分享讨论啊。
推荐阅读
小果教你用TransDecoder轻松预测蛋白开放阅读框序列

shengxinguoer
生信果
生信硬核知识解答
和小果一起学生信
